Instalando o FastQC
Instalando o FastQC
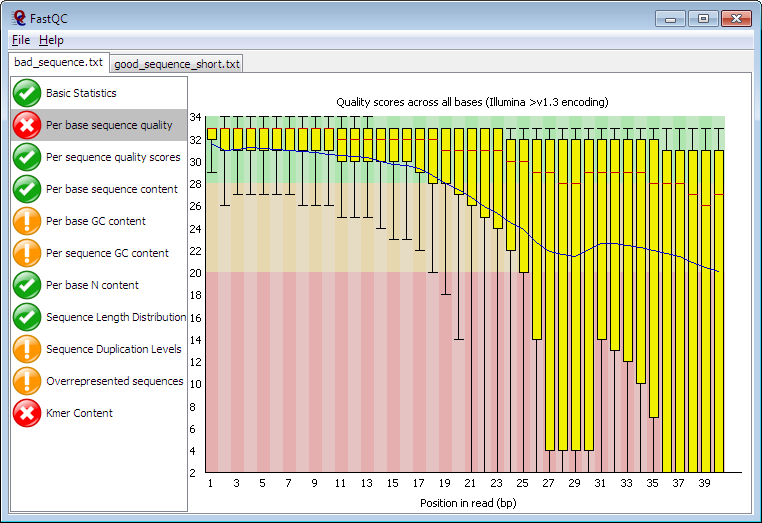
O FastQC é um software que permite visualizar a qualidade das bases de uma amostra sequenciada. Além disso, também permite verificar algumas outras métricas de qualidade do sequenciamento, como presença de contaminantes, sequências artefatos, frequência de nucleotídeos, etc.
Se você utiliza Ubuntu ou o WSL2 no Windows, abra um terminal e digite o seguinte comando:
sudo apt-get install fastqc
Se você utiliza Mac, abra um terminal e digite o seguinte comando:
brew install fastqc
Após instalado, para rodar o FastQC em um arquivo Fastq, rode o seguinte comando:
fastqc [arquivo.fastq]
Substituta o termo arquivo.fastq pelo caminho até o arquivo que você deseja analisar.